L’ingegneria genetica determina la sequenza di basi e viene utilizzata per la costruzione di organismi geno-tipicamente modificati: OGM.
La prima molecola prodotta con l’ingegneria genetica è stata l’insulina, prodotta da batteri OGM che diventano micro fabbriche farmacologiche.
La costruzione degli OGM si basa sul fatto che il codice genetico è universale, è valido sia per i batteri che per gli eucarioti animali e vegetali, perché deriva direttamente dalla prima cellula procariota apparsa sulla Terra.
La prima tecnica per realizzare organismi genotipicamente modificati prevedeva l’utilizzo degli enzimi di restrizione, oggi si è passati alla tecnica CRISPR/Cas9.
Con gli OGM si curano malattie dell’uomo e delle piante, si aumenta le produzioni vegetali,… con il sequenziamento del genoma si accerta la paternità di un figlio e si scova il malfattore che ha lasciato il suo DNA sulla scena del delitto.
Enzimi di restrizione
Studiando i batteri del suolo si scopre che ci sono dei pezzi di DNA batterico che si ripetono, e si ritrovano identici in molti batteri anche molto diversi fra loro. Si scopre che questi pezzi di DNA sono dei pezzi di virus assimilati del DNA batterico. Questi pezzi virali diventano la memoria immunitaria dei batteri. Se uno di questi virus entra nel batterio e viene riconosciuto, viene disattivato tagliandolo. Questa memoria viene mantenuta anche durante la riproduzione batterica. A questo punto si pensa di utilizzare questa capacità di taglio del DNA in posizioni specifiche con gli Enzimi di restrizione.
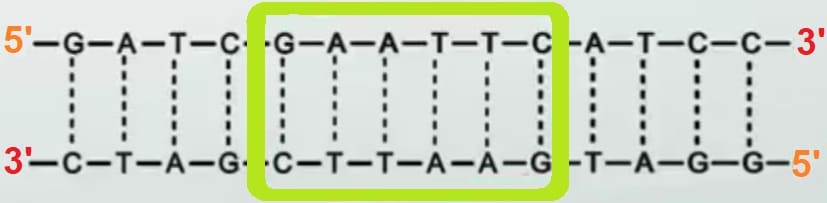
Gli Enzimi di restrizione tagliano pezzi di DNA o RNA in corrispondenza di sequenze palindrome tipo ANNA, leggibili indistintamente da sin a dex che da dex a sin , da 5′ a 3′ come da 3′ a 5′. Sono enzimi che naturalmente vengono usati dai batteri per difendersi dai virus, tagliando i loro acidi nucleici. Il taglio avviene solo su una sequenza e non su tutte, perché così il batterio evita di tagliare il suo patrimonio genetico, ma taglia solo quello virale.
Esistono due tipi di Enzimi di restrizione: le esonucleasi e le endonucleasi. Questi enzimi tagliano il DNA, cioè rompono il legame estere-fosforico tra il ribosio e il gruppo fosfato della catena di DNA.
Le esonucleasi tagliano il DNA all’estremità. Le esonucleasi vengono usate dalle cellule in duplicazione per correggere errori di duplicazione.
Le endonucleasi tagliano il DNA nel mezzo.
L’ingegneria genetica non è interessata alle esonucleasi ma alle endonucleasi.
Ogni tipo di endonucleasi può tagliare solo in un sito, infatti esistono più endonucleasi-forbici, esiste un set di forbici. Come si fa a prendere la forbice giusta, con un setaccio molecolare: l’elettroforesi.
Il taglio della sequenza palindroma, rende poi più facile la ricostruzione sia in un senso che nell’altro.
Le endonucleasi possono tagliare in due modi: piatto o sfalsato. Il taglio sfalsato permette l’introduzione del gene umano nel gene batterico, più precisamente nel plasmidio batterico.
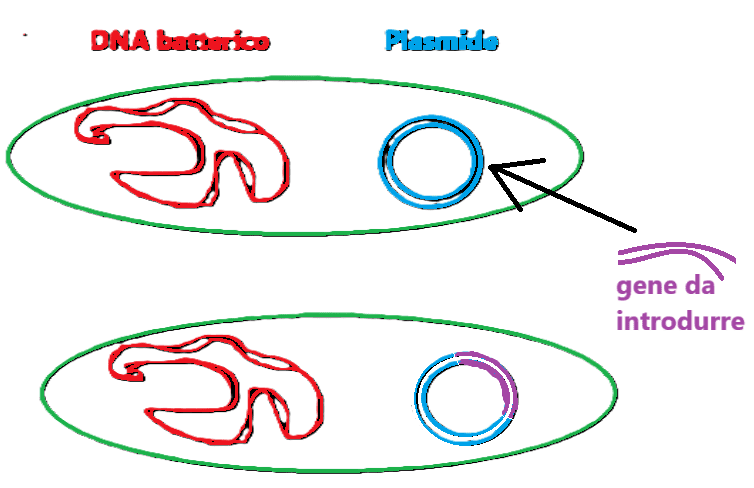
I tagli effettuati sono due: uno sulla cellula donante e uno sulla cellula ricevente, per inserire nel genoma del plasmide il gene umano. I tagli vengono compiuti dalla stessa endonucleasi, dallo stesso enzima di restrizione.
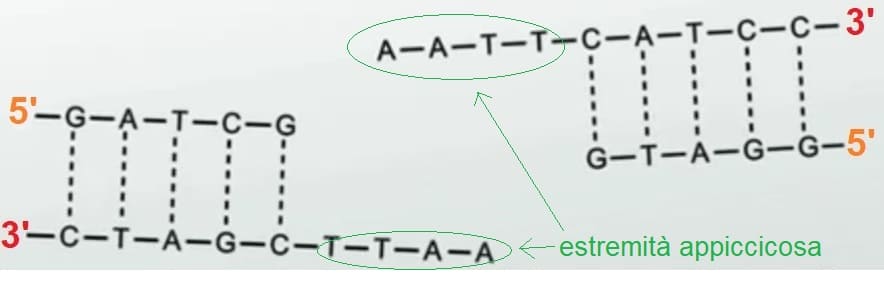
Il taglio è sfalsato, cioè dal taglio abbiamo per un breve tratto un solo filamento.
Le 4 basi libere dell’esempio sopra si incontrano con altre 4 basi complementari libere, così è possibile la ricostruzione del doppio filamento, certo con l’aiuto di una dna-ligasi.
Il primo gene umano trasferito è stato quello che produce l’insulina umana. Il batterio ora produce insulina umana, successivamente l’insulina viene estratta per essere poi iniettata ai pazienti.
PCR
La PCR è l’acronimo di reazione a catena della polimerasi.
La PCR duplica all’infinito un gene.
Per riprodurre un gene, basta conoscere i primi 5 e gli ultimi 5 nucleotidi, testa e coda, del gene da esaminare: i primers.
In una provetta si aggiungono il gene da duplicare, i primers, i nucleotidi necessari, e una dna-polimerasi.
La polimerasi usa il modello del gene per ricopiarlo, inizia il lavoro agganciando il primers iniziale, continua agganciando i singoli nucleotidi, e finisce il lavoro con il primers finale.
Per raggiungere il gene, bisogna aprire le eliche, riscaldando a 95°C, a 50°C i primers si agganciano alla polimerasi e a 70°C l’enzima lavora, cioè duplica il DNA. Dopo un ciclo ho raddoppiato il gene.
Se si fanno 30 cicli, caldo-freddo, si produrrà 2^30 geni uguali ( 2 perchè produco una coppia e 30 sono i cicli), circa un miliardo di geni uguali.
CRISPR/Cas9
La tecnica CRISPR/Cas9 (crisper) é rivoluzionaria.
La CRISPR/Cas9 è una taglia e cuci del DNA.
Un RNA specifico ricerca il gene, e un enzima lo taglia all’inizio e alla fine per estrarlo dal DNA.
Con questa tecnica è possibile sostituire un gene all’interno della catena del nostro DNA, sostituire un gene malato con un gene sano, un gene ipoproduttivo con uno iperproduttivo,…
Il problema è ricercare il punto esatto in cui si trova il gene all’interno della molecola di DNA che è composta da 3 miliardi di basi. Come cercare un ago in un pagliaio, in questo caso il pagliaio sono le milioni di combinazioni possibili.
La ricerca del gene avviene con un RNA complementare al tratto del DNA ricercato. Questo polinucleotide è composto da solo 20 nucleotidi. Sapendo che 4 sono i nucleotidi, il calcolo combinatorio farà 4^20, quindi milioni di combinazioni. Quindi con soli 20 nucleotidi ritrovo il famoso ago nel pagliaio.
Trovato il gene giusto, si apre il DNA scaldandolo, a questo punto un enzima legato all’RNA (ricercatore) taglia il gene “malato”. Il DNA si trova spezzato in due parti, è un momento critico della cellula che attiva dei sistemi per riparare il DNA. I filamenti hanno delle estremità libere o “appiccicose”. Adesso si inserisce nella cellula il gene “sano” con estremità “appiccicose” e voilà gli enzimi cellulari riparativi aggiustano la cellula.
Abbiamo un DNA “nuovo” nel senso che prima non c’era, indistinguibile dai DNA naturali, e perciò è impossibile dire a posteriori che quella cellula è OGM.
L’RNA complementare che ha svolto la ricerca del punto del taglio si chiama CRISPR, si tratta di un oligonucleotide (20) che può essere costruito e spedito per posta in tutto il mondo al prezzo di poche decine di euro.
L’enzima che taglia il doppio filamento di DNA si chiama Cas9.
La tecnica, così com’è, può funzionare solo nel caso delle cellule del sangue e nei gameti, ma non nelle cellule dei tessuti solidi, come il cervello, il fegato, il polmone, ecc.
Prima malattia curata con CRISPR/Cas9
La prima cellula “malata” che ha subito la tecnica CRISPR/Cas9 è stata una cellula affetta da anemia falciforme o mediterranea. La cellula “malata” è stata “guarita” e riniettata nel paziente guarendolo. Lo stesso si potrebbe fare sugli ovuli e gli spermatozoi, che poi potrebbero essere utilizzati nella fecondazione in vitro, e quindi generare persone che non portano più quel “difetto” genetico.
Ora c’è una possibilità anche per i tessuti solidi con delle tecniche di consegna precisa.
La consegna dell’OGM
Fatta la modifica genetica, occorre che sia consegnata nel posto giusto, cioè alla cellula giusta, come la consegna a casa della pizza.
Il nuovo DNA prodotto in laboratorio si potrebbe introdurre nelle cellule di cervello, fegato, polmone, ecc infettandole con un virus dell’HIV/AIDS.
Il virus dell’HIV/AIDS viene svuotato del suo patrimonio genetico che viene sostituito con il nuovo DNA.
Controindicazioni
Tuttavia accade che l’enzima commetta degli errori, tagliando un gene sano della cellula malata. L’errore commesso è difficilmente rilevabile, l’errore può causare nel tempo gravi conseguenze al paziente.
Un’altra domanda che deve trovare risposta: se cambiando un gene sicuramente risolviamo un problema, non è detto che non compaiano nuove malattie, anche perché non conosciamo in modo completo l’espressione di taluni caratteri dati dal coinvolgimento di più geni, e se un giorno comparisse un Sagittario: un centauro metà uomo e metà cavallo.
Sequenziamento genetico
L’ingegneria genetica è in grado di sequenziare il patrimonio genetico di un individuo, cioè riesce a dire esattamente la sequenza di basi che formano un filamento di DNA o RNA.
La tecnica di sequenziamento di Singer
La tecnica si basa su 4 nucleotidi che hanno subito una doppia modifica: sono stati marcati per essere riconosciuti e manca un gruppo ossidrile sullo zucchero, per cui quando si aggancerà il nucleotide modificato, la polimerasi non sarà più in grado di continuare il lavoro e il filamento sarà incompleto.
Con la PCR si riproduce un gran numero di filamenti di DNA che faranno da modello, si aggiunge una gran quantità dei 4 diversi nucleotidi, e una piccola quantità dei 4 nucleotidi modificati, in rapporto 1/10, si aggiungono i primers, e l’enzima dna-polimerasi.
Il risultato sarà la formazione di tanti neo filamenti di lunghezza diversa, dove l’ultimo nucleotide è marcato e quindi riconoscibile.
I filamenti prodotti vengono fatti correre su una matrice di gel per essere separati con l’elettroforesi per essere studiati.
Elettroforesi dei geni
I differenti filamenti di DNA vengono messi in gel di agarosio, al gel si attaccano degli elettrodi, in modo da aversi un polo positivo e un polo negativo. Si immette un flusso di corrente elettrica che coinvolge anche i filamenti.
I filamenti di DNA hanno carica negativa, la corrente elettrica spinge il DNA verso il polo positivo. I filamenti più corti corrono più velocemente dei filamenti lunghi. Il filamento più corto porta il primo nucleotide marcato, il secondo filamento porta il secondo nucleotide, e così via, finchè il filamento più lungo porterà l’ultimo nucleotide, anch’esso marcato.
Sul gel appare un disegno a bande. Le bande emettono segnali. Il segnale radioattivo o fluorescente permette di distinguere le 4 diverse basi che costituiscono il nuovo filamento.
Così con l’ingegneria genetica è possibile ricostruire la sequenza nucleotidica completa.
Ogni disegno è caratteristico di una persona, come le impronte digitali, e quindi si riesce a risalire al soggetto. Questa tecnica è usata per gli esami di paternità e per la criminologia.
Con il sequenziamento è possibile il riconoscimento dei virus nel corso delle epidemie e quindi prendere provvedimenti di sanità pubblica, ad esempio la necessità di costruire un vaccino per la profilassi.
Vaccini a mRNA
L’ultimo strumento nella lotta ai virus è il vaccino mRNA. Si prendono dei tratti del virus mRNA, come il virus del Coronavirus Sars-Cov-2, non tutto l’mRNA virale. Si isolano solo i geni virali che sintetizzano una specifica proteina: la spike. La spike è la molecola che durante l’infezione naturale aggancia il virus alle cellule dell’ospite, cioè alle cellule delle vie respiratorie umane. Il vaccino mRNA viene iniettato nell’uomo, il pezzetto di mRNA virale entra nelle cellule umane, i ribosomi sintetizzano solo la proteina spike. La cellula umana non viene danneggiata dal vaccino, ma libera la proteina spike che il sistema immunitario umano riconosce come estranea. Ora le difese sono allertate ed inizia la produzione di anticorpi contro la spike dell’ eventuale virus di strada.
Ingegneria genetica nei neonati
Nei neonati si controllano 60 malattie eseguendo un esame del sangue del tallone, ma l’ingegneria genetica permette il controllo di altre 700 malattie genetiche rilevabili con il sequenziamento. Ad esempio dal controllo dei geni BRCA1 e BRCA2 si può sapere se siamo predisposti al rischio di cancro al seno, all’ovaio, alla prostata e al pancreas. BRCA1 e BRCA2 sono importanti per la riparazione di un DNA danneggiato o difettoso per una replicazione errata.